问题1:spacing从(0.5,0.5,0.5)-> (1,1,1)发生了什么变化?
图像被降采样,分辨率降低 ,体素变大了一倍。
公式为:新像素个数 × 新的间距 = 原来的间距 × 原来的像素个数
问题2:当前是怎么做crop的?要修改crop应该怎么做
用 create_nonzero_mask 非零的位置加入掩码,用 crop_to_nonzero 裁剪数据,只保留包含非零区域的 bounding box。目的是去掉大量的黑色背景。最后通过np.get_bbox函数获取分割图像的前景区域,并将所有非零值赋0,为0的值赋-1。
修改crop的方法:有时候想给目标周围多留几个像素,就需要扩大边界,支持 margin 是一种修改,还有 target_shape 支持裁剪后固定的某个形状,可以 padding 可以截断。
问题3:使用的哪个归一化函数?
直接运行程序,print 打印显示使用的 ‘ZScoreNormalization’ 归一化函数
default_resampling.py
路径:nnunetv2/preprocessing/resampling/default_resampling.py
- get_do_separate_z:判断是否需要处理 z 轴,具体为 max(spacing) ÷ min(spacing) ,再和 anisotropy_threshold 比较,如果前者大,则单独处理 z 轴;如果后者大,则不单独处理。这里提到一个“各向异性”,就是xyz的差距是否过大。
1
2
3
4
5
6
| def get_do_separate_z(
spacing: Union[Tuple[float, ...], List[float], np.ndarray],
anisotropy_threshold=ANISO_THRESHOLD):
# 计算“最大像素间距 ÷ 最小像素间距”,如果大于阈值,就单独处理Z轴
do_separate_z = (np.max(spacing) / np.min(spacing)) > anisotropy_threshold
return do_separate_z
|
1
2
3
4
5
| def get_lowres_axis(
new_spacing: Union[Tuple[float, ...], List[float], np.ndarray]):
# 找到哪个轴是各向异性的(那个方向就是精度最低的)
axis = np.where(max(new_spacing) / np.array(new_spacing) == 1)[0] # find which axis is anisotropic
return axis
|
- compute_new_shape:比较实用的函数,根据新旧像素间距,计算数据缩放后的新尺寸。其中 old_shape 是数据原来的像素尺寸;old_spacing 是数据原来的像素间距;new_spacing 是想要的新像素间距(;new_shape 是计算后的数据新像素尺寸。
1
2
3
4
5
6
7
8
9
10
| def compute_new_shape(old_shape: Union[Tuple[int, ...], List[int], np.ndarray],
old_spacing: Union[Tuple[float, ...], List[float], np.ndarray],
new_spacing: Union[Tuple[float, ...], List[float], np.ndarray]) -> np.ndarray:
# 检查1:旧 spacing 方向数,必须和旧 shape 方向数一样
assert len(old_spacing) == len(old_shape)
# 检查2:新 shape 方向数,必须和旧 shape 方向数一样
assert len(old_shape) == len(new_spacing)
# 公式:计算每个方向的新像素数,最后转成整数
new_shape = np.array([int(round(i / j * k)) for i, j, k in zip(old_spacing, new_spacing, old_shape)])
return new_shape
|
举个例子:
原来的尺寸 old_shape = (128, 128, 64)(X=128像素,Y=128像素,Z=64像素);
原来的间距 old_spacing = (2, 2, 4)(X/Y轴每像素2毫米,Z轴每像素4毫米);
想要的新间距 new_spacing = (1, 1, 2)(X/Y轴每像素1毫米,Z轴每像素2毫米)。
公式为:实际物理大小 = 像素个数 × 像素间距;缩放后,实际物理大小不能变,所以:新像素个数 × 新的间距 = 原来的间距 × 原来的像素个数 。然后利用这个公式逐个方向计算(结果取整数),返回 new_shape 的值。
- determine_do_sep_z_and_axis:决定要不要单独处理低精度轴?以及具体处理哪个轴?
1
2
3
4
5
6
7
8
9
10
11
12
13
14
15
16
17
18
19
20
21
22
23
24
25
26
27
28
29
30
31
32
33
34
35
36
37
38
| def determine_do_sep_z_and_axis(
force_separate_z: bool, # 手动强制执行“是否单独处理z轴”
current_spacing, #数据当前的像素间距
new_spacing, #数据想要改成的新像素间距
separate_z_anisotropy_threshold: float = ANISO_THRESHOLD) -> Tuple[bool, Union[int, None]]:
# 判断是否强制
if force_separate_z is not None:
do_separate_z = force_separate_z # 直接用指定的
# 如果指定要处理
if force_separate_z:
# 找现在数据的低精度轴
axis = get_lowres_axis(current_spacing)
else:
axis = None
else:
# 情况1:current_spacing 是各向异性,则找现在的低精度轴
if get_do_separate_z(current_spacing, separate_z_anisotropy_threshold):
do_separate_z = True
axis = get_lowres_axis(current_spacing)
# 情况2:current_spacing 没问题,但 new_spacing 是各向异性,则找新间距的低精度轴
elif get_do_separate_z(new_spacing, separate_z_anisotropy_threshold):
do_separate_z = True
axis = get_lowres_axis(new_spacing)
# 情况3:现在和新间距都没问题,则不处理
else:
do_separate_z = False
axis = None
if axis is not None: # 如果找到了要处理的轴
if len(axis) == 3: # 3个轴都是低精度
do_separate_z = False # 不处理
axis = None
elif len(axis) == 2: # 2个轴是低精度
do_separate_z = False # 不处理
axis = None
else: # 只有1个轴是低精度
axis = axis[0] # 取这个轴的编号
return do_separate_z, axis
|
- resample_data_or_seg_to_spacing:把数据(或分割标签)按照新旧像素间距,精准缩放成新的尺寸,还会根据之前判断的 “是否单独处理低精度轴” 来选择最优的缩放方式,保证缩放后数据不失真、物理大小不变。
1
2
3
4
5
6
7
8
9
10
11
12
13
14
15
16
17
18
19
20
| def resample_data_or_seg_to_spacing(data: np.ndarray, #要缩放的原始数据
current_spacing: Union[Tuple[float, ...], List[float], np.ndarray], #数据当前的像素间距
new_spacing: Union[Tuple[float, ...], List[float], np.ndarray], #想要的新像素间距
is_seg: bool = False, #是不是分割标签的开关
order: int = 3, #普通数据的缩放算法等级(默认3,代表用三次插值,缩放后细节保留得好,适合影像数据)
order_z: int = 0, #单独处理 Z 轴时的缩放算法等级(默认0,代表最近邻插值,适合低精度轴,避免失真)
force_separate_z: Union[bool, None] = False, #强制处理z轴
separate_z_anisotropy_threshold: float = ANISO_THRESHOLD): #判断各向异性的阈值
# 是否单独处理?处理哪个轴?
do_separate_z, axis = determine_do_sep_z_and_axis(force_separate_z, current_spacing, new_spacing,
separate_z_anisotropy_threshold)
# 检查数据格式是否满足4维
if data is not None:
assert data.ndim == 4, "data must be c x y z"
# 计算数据的新尺寸
shape = np.array(data.shape) # 先拿到原始数据的尺寸
new_shape = compute_new_shape(shape[1:], current_spacing, new_spacing)
# 执行缩放
data_reshaped = resample_data_or_seg(data, new_shape, is_seg, axis, order, do_separate_z, order_z=order_z)
return data_reshaped
|
resample_data_or_seg:按新尺寸,用合适的算法,真正把数据(或分割标签)缩放到位,支持单独处理低精度轴,保证缩放后数据不失真。
参数具体如下:
data:要缩放的原始数据;
new_shape:要缩放成的新尺寸(比如 256×256×128);
is_seg:是不是分割标签(True=是标签,False=普通影像);
axis:要单独处理的低精度轴(比如 2=Z轴,None=不单独处理);
order:普通缩放的算法等级(默认3,三次插值,保细节);
do_separate_z:要不要单独处理低精度轴(True=要,False=不要);
order_z:单独处理轴时的算法(默认0,最近邻插值,保精度);
dtype_out:输出数据的格式(默认和原始数据一样)。
cropping.py
1
2
3
4
5
6
7
8
9
10
11
12
13
14
15
16
17
18
19
20
| def create_nonzero_mask(data):
"""
:param data:形状为 (C, X, Y, Z) 或 (C, X, Y) 的多通道医学图像 C = 通道数
:return: the mask is True where the data is nonzero
"""
assert data.ndim in (3, 4),
# 用第 0 个通道初始化掩码:非零的位置标记为 True
nonzero_mask = data[0] != 0
# 遍历剩下的通道,将它们非零的位置加入掩码
for c in range(1, data.shape[0]):
nonzero_mask |= data[c] != 0
# |= 的意思是:mask = mask OR (data[c] != 0)
'''
返回值:
一个布尔值数组,shape 为 (X, Y, Z)
True 代表该位置至少有一个通道不是0(有内容)
False 代表所有通道都是0(背景)
'''
# 填洞 binary_fill_holes,应该是为了保证实心
return binary_fill_holes(nonzero_mask)
|
default_normalization_schemes.py
路径:nnunetv2/preprocessing/normalization/default_normalization_schemes.py
1
2
3
4
5
6
| class ImageNormalization(ABC)...
class ZScoreNormalization(ImageNormalization)...
class CTNormalization(ImageNormalization)...
class NoNormalization(ImageNormalization)...
class RescaleTo01Normalization(ImageNormalization)...
class RGBTo01Normalization(ImageNormalization)...
|
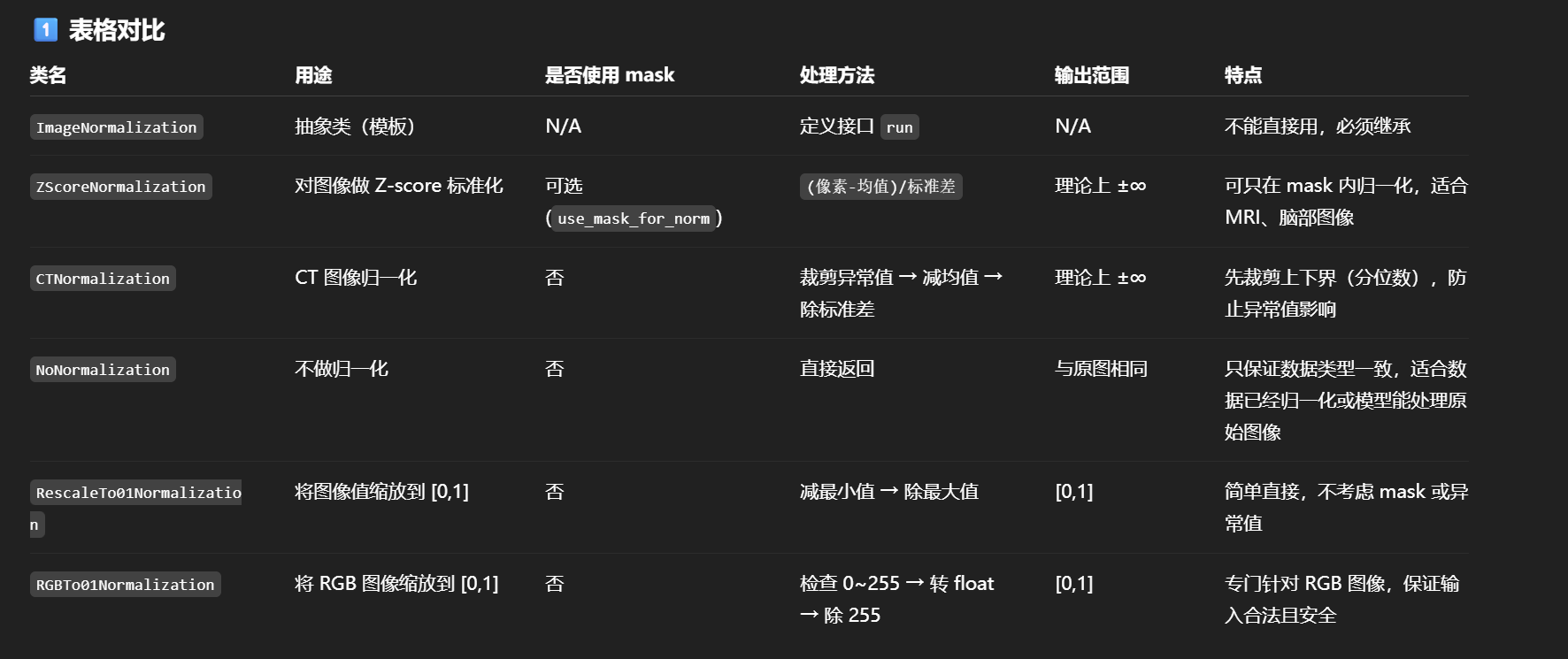
这部分就是归一化函数的类定义,具体情况具体分析
